Multi Vector and Dataset Geometry
TL;DR
Multi-vector retrieval 알고리즘 선택은 **유사도 함수(MaxSim/SumSim/Top-K Sum)**와 데이터 기하학(Isotropic/Anisotropic/Multi-Kernel) 두 축에 의해 결정된다. PLAID는 moderate variance + MaxSim 조합에, MUVERA는 isotropic 데이터에 최적화되어 있으며 이 조건을 벗어나면 성능이 급격히 저하된다. 흥미롭게도 SumSim은 mean-pooling으로 단일 벡터 MIPS로 환원 가능하며, ColPali는 per-token HNSW + 이진화로 32배 압축하면서도 94% recall을 유지할 수 있다. 임베딩 모델 학습 시 variance/isotropy 정규화를 통해 인덱싱 친화적 기하학을 설계할 수 있다는 점이 핵심이다.
Key Takeaways
- 알고리즘 선택 전 데이터 기하학 분석이 필수: PLAID/MUVERA 도입 전에 intra-document variance와 anisotropy 정도를 정량화하라. 잘못된 조합은 centroid pruning 붕괴나 recall 저하를 초래한다.
- SumSim은 특수 인프라가 불필요: 내적의 bilinearity를 활용하면 mean-pooled 단일 벡터 MIPS로 환원되어 표준 HNSW/DiskANN으로 처리 가능하다.
- ColPali의 고정 cardinality는 게임 체인저: 1030개 고정 패치는 per-token HNSW + 이진화(32x 압축)로 효율적 처리가 가능하며, ~94% recall을 유지한다.
- Contrastive learning이 기하학을 결정: InfoNCE 손실의 온도 파라미터와 hard negative mining이 multi-kernel anisotropic 분포를 생성하며, 이것이 인덱싱 효율성에 직접 영향을 미친다.
- 모델 설계와 인덱싱은 독립적이지 않음: 학습 단계에서 variance/isotropy 정규화를 통해 PLAID나 MUVERA에 최적화된 임베딩 분포를 유도할 수 있다. 이는 PoBE(Preference-Optimized Binary Embedding) 같은 접근에 직접 활용 가능하다.
상세 내용
Multi-Vector Retrieval의 두 가지 핵심 축
전통적인 retrieval은 point-to-point MIPS(Maximum Inner Product Search)로 해결되지만, multi-vector retrieval은 본질적으로 집합 대 집합(set-to-set) 유사도 문제다. 각 문서와 쿼리는 단일 벡터가 아닌 임베딩 집합으로 표현된다: Q = {q₁, ..., qₘ}, P = {p₁, ..., pₙ}.
이 문제 공간은 두 개의 독립적인 축으로 분류할 수 있다:
- 유사도 함수(Similarity Function): 두 집합 간 유사도를 계산하는 방법
- 데이터 기하학(Dataset Geometry): 임베딩 공간 내 분포의 통계적 구조
대부분의 기존 논의는 MaxSim + ColBERT 스타일 분포라는 단일 조합에 집중되어 있으며, 이는 전체 문제 공간의 일부에 불과하다.
유사도 함수의 분류 체계
MaxSim (Chamfer Similarity)
ColBERT의 표준 접근법으로, 각 쿼리 토큰에 대해 가장 잘 매칭되는 문서 토큰을 찾아 합산한다:
sim_MaxSim(Q, P) = Σᵢ max_j ⟨qᵢ, pⱼ⟩
- 비대칭적: 쿼리 토큰에 대해서만 합산 (문서→쿼리 방향은 고려하지 않음)
- Fine-grained alignment: 각 쿼리 토큰이 독립적으로 최적 매칭을 찾음
- Winner-takes-all 특성: 각 쿼리 토큰에 대해 단 하나의 문서 토큰만 기여
SumSim (All-Pairs)
모든 가능한 쿼리-문서 토큰 쌍의 유사도를 합산한다:
sim_SumSim(Q, P) = Σᵢ Σⱼ ⟨qᵢ, pⱼ⟩
- 대칭적: 모든 토큰이 동등하게 기여
- Cross-modal matching, group recommendation 등에 사용
- PLAID의 pruning 전략과 근본적으로 비호환
Top-K Sum
각 쿼리 토큰에 대해 상위 k개 문서 토큰의 유사도를 합산:
sim_TopK(Q, P) = Σᵢ Σ(j∈TopK) ⟨qᵢ, pⱼ⟩
- MaxSim (k=1)과 SumSim (k=|P|) 사이의 중간 지대
- k 증가 시 PLAID의 centroid pruning 효율성 감소
Symmetric Chamfer
양방향 MaxSim의 평균:
sim_SymChamfer(Q, P) = 1/2 [sim_MaxSim(Q, P) + sim_MaxSim(P, Q)]
저자의 핵심 지적: 현재 multi-vector retrieval 담론은 MaxSim을 문제 자체와 동일시하고 있으며, 다른 유사도 함수들은 체계적으로 무시되고 있다.
Dataset Geometry: 세 가지 기하학적 체제
임베딩 분포의 통계적 구조는 인덱싱 알고리즘의 성능을 근본적으로 결정한다.
Gaussian Isotropic
모든 방향에서 균일한 분산을 가진 분포:
v ~ N(μ, σ²I)
- 이론적 분석에서 자주 가정되지만 실제로는 드묾
- 랜덤 하이퍼플레인 기반 LSH가 이론적 보장을 제공하는 체제
Gaussian Anisotropic
방향에 따라 분산이 다른 분포:
v ~ N(μ, Σ), Σ ≠ σ²I
- 특정 방향(주성분)으로 데이터가 "늘어난" 형태
- SimHash 같은 각도 기반 해싱에 문제 발생
Multi-Kernel Anisotropic
여러 Gaussian 클러스터의 혼합, 각 클러스터가 비등방적:
v ~ Σₖ πₖ · N(μₖ, Σₖ)
- 실제 학습된 임베딩의 현실적 분포
- ColBERTv2, ColPali 등이 이 체제에 속함
- Contrastive learning의 자연스러운 결과물
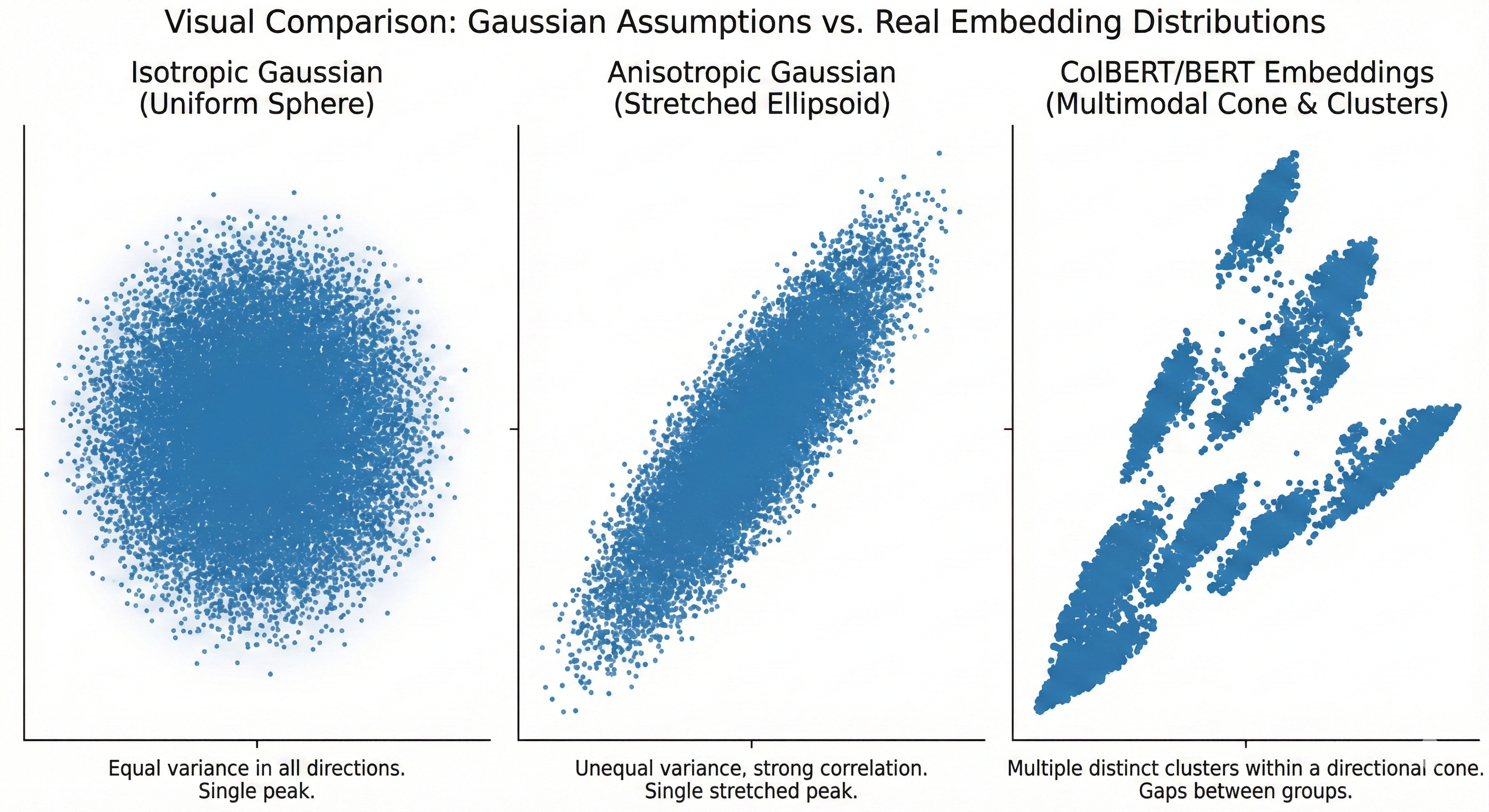
세 가지 기하학적 체제의 비교. 실제 multi-vector 임베딩은 Multi-Kernel Anisotropic 체제에 해당한다.
Contrastive Training이 만드는 기하학
ColBERT의 InfoNCE 손실 함수는 특정 기하학적 구조를 유도한다:
온도 파라미터 τ의 역할
L_InfoNCE = -log [exp(⟨q, p⁺⟩/τ) / Σᵢ exp(⟨q, pᵢ⟩/τ)]
- τ는 클러스터 tightness를 제어하는 파라미터
- 낮은 τ → 더 촘촘한 클러스터 (equi-angular 형태)
- 높은 τ → 더 넓게 퍼진 분포
Hard Negative Mining의 영향
의미적으로 유사하지만 관련 없는 문서(hard negatives)를 명시적으로 구분하도록 학습하면:
L_hard = -log [exp(⟨q, p⁺⟩/τ) / (exp(⟨q, p⁺⟩/τ) + λ·Σ exp(⟨q, p⁻_hard⟩/τ))]
- 클러스터 간 경계 방향으로 방향성 늘어남(directional stretching) 발생
- Within-kernel 공분산이 비구형(non-spherical)이 됨
- 결과적으로 multi-kernel anisotropic 분포 생성
핵심 통찰: 하나의 금융 문서 내에서도 토큰들은 여러 의미적 역할(전문 용어, 기능어, 맥락 수식어)을 수행하며, 각각이 임베딩 공간의 다른 영역(다른 커널)에 매핑된다.
기하학 정량화 지표
Intra-document variance (문서 내 분산)
σ²_intra(d) = 1/|P_d| Σᵢ ‖pᵢ - μ_d‖²
μ_d = 1/|P_d| Σᵢ pᵢ
- 높은 variance: 토큰들이 여러 의미 영역에 분산
- PLAID의 centroid pruning 효율성에 직접 영향
Residual magnitude (잔차 크기)
centroid 할당 후 잔차:
r_i = p_i - c_assigned(i)
- 큰 잔차: 양자화 시 재구성 노이즈 증가
- PLAID Stage 3의 신뢰도에 영향
문서별 intra-document variance 분포. ColPali 같은 vision 모델은 텍스트 모델보다 훨씬 높은 분산을 보인다.
PLAID의 기하학적 한계
PLAID는 3단계 파이프라인으로 작동한다:
- Centroid Pruning: 쿼리 토큰과 관련 없는 centroid 제거
- Document Filtering: 관련 centroid만 포함한 문서로 후보 축소
- Verification: 압축된 표현으로 정확한 MaxSim 계산
Centroid Pruning의 선택성 붕괴
문서 d가 활성화하는 고유 centroid 수:
n_d = |{c_i : ∃p ∈ P_d, c_i = argmin_c ‖p - c‖}|
PLAID의 선택성(제거되는 문서 비율):
selectivity = 1 - (n_d · n_query) / (C · N_docs)
- 높은 σ²_intra (예: ColPali) → n_d가 크게 증가
- C = 65,536인 경우, n_d가 수천 개로 증가하면 pruning이 거의 아무것도 제거하지 못함
- 결과: 거의 모든 문서가 Stage 2로 진입 → 계산 비용 급증
SumSim에서의 PLAID 붕괴
MaxSim의 "winner-takes-all" 특성:
- 각 쿼리 토큰에 대해 단 하나의 문서 토큰만 승리
- 비매칭 centroid는 max 연산에서 무시됨
SumSim의 "all-contribute" 특성:
- 모든 문서 토큰이 모든 쿼리 토큰에 기여
- Centroid pruning의 상한 기반 제거가 무의미해짐
PLAID Stage 2의 pruning 로직:
if max_i ⟨q_i, c_k⟩ < θ → centroid c_k 제거
이는 MaxSim에서만 유효하며, SumSim에서는:
contribution(c_k) = Σᵢ Σ(p∈cluster_k) ⟨qᵢ, p⟩
단일 쿼리 토큰과의 최대 유사도로 전체 기여를 상한할 수 없음.
Quantization 품질과 Residual Magnitude
ColBERTv2는 centroid ID + 2-bit 양자화 잔차로 압축:
재구성 오차: ‖p_i - (c_i + r_q)‖
MaxSim 근사 오차: |MaxSim_true - MaxSim_approx| ≤ Σᵢ ‖ε_i‖
MaxSim에서는 이것이 유효하지만, large residual을 가진 anisotropic 데이터에서는 2-bit 양자화가 significant noise를 도입한다.
Residual magnitude 분포. 큰 잔차는 양자화 노이즈를 증가시켜 PLAID의 정확도를 저하시킨다.
MUVERA의 기하학적 한계
MUVERA는 SimHash 기반 파티셔닝으로 multi-vector 집합을 고정 차원 벡터(FDE)로 변환한다.
SimHash와 Anisotropy의 불협화음
b개의 랜덤 하이퍼플레인 {h₁, ..., h_b}를 사용. Isotropic 데이터에서 충돌 확률:
P_collision(u, v) = 1 - θ_uv/π
이는 각도만으로 결정되며, 균일 분포에서 이론적 보장이 성립한다.
그러나 Anisotropic 데이터에서는:
Σ = [σ₁² 0; 0 σ₂²], σ₁² >> σ₂²
주축(high variance 방향) u에 수직인 랜덤 하이퍼플레인이:
- ℓ₂ 거리에서 가까운 두 벡터를 다른 버킷으로 분리
- 유효 각도 θ_eff > θ_uv
Anisotropic 클러스터에서 SimHash의 문제. 주축에 수직인 하이퍼플레인이 가까운 이웃을 분리한다.
Over-Partitioning 문제
올바른 충돌 확률:
P_collision^(b) = (1 - θ_eff/π)^b
b에 대해 지수적으로 감소하여, 큰 b (fine-grained FDE)는 nearest neighbor 쌍을 다른 파티션으로 분리할 확률이 높아진다.
트레이드오프 딜레마:
- 작은 b: coarse FDE → 낮은 discrimination, 많은 false positive
- 큰 b: fine-grained FDE → nearest neighbor 분리, recall 저하
Multi-kernel anisotropic 공간에서 elongated within-kernel 분포는 SimHash의 이론적 보장을 무효화한다.
실용적 해결책 #1: SumSim은 Mean-Pooling으로 충분하다
내적의 **bilinearity (쌍선형성)**를 활용한 핵심 증명:
sim_SumSim(Q, P) = Σᵢ Σⱼ ⟨qᵢ, pⱼ⟩
= Σᵢ Σⱼ qᵢᵀpⱼ
= (Σᵢ qᵢ)ᵀ (Σⱼ pⱼ)
= |Q| · |P| · ⟨μ_Q, μ_P⟩
여기서 μ_Q = (1/|Q|)Σᵢ qᵢ, μ_P = (1/|P|)Σⱼ pⱼ
SumSim이 mean-pooled 벡터 간 단일 내적으로 환원되는 과정.
실무 함의:
- SumSim 기반 retrieval (aggregate affinity, group recommendation, cross-modal matching)
- Mean-pooled representation을 오프라인 계산
- 표준 ANN 시스템으로 인덱싱: HNSW, DiskANN, ScaNN
- PLAID도, MUVERA도, 커스텀 인프라도 불필요
코드 예시:
# Multi-vector 대신 단일 벡터로 변환
doc_embedding_pooled = doc_embeddings.mean(dim=0)
query_embedding_pooled = query_embeddings.mean(dim=0)
# 표준 HNSW 인덱스 사용
index = hnswlib.Index(space='ip', dim=embedding_dim)
index.add_items(doc_embeddings_pooled)
results = index.knn_query(query_embedding_pooled, k=10)
# 필요 시 full multi-vector로 re-rank
for doc_id in results:
exact_score = compute_sumsim(query_embeddings, doc_embeddings[doc_id])
실용적 해결책 #2: ColPali의 고정 Cardinality 활용
ColPali는 ColBERT와 근본적으로 다른 특성을 가진다:
- ColBERT: 텍스트 길이에 따라 가변적인 토큰 수 (50~500+)
- ColPali: 페이지당 정확히 1030개 임베딩 (1024 image patches + 6 instruction tokens)
이 고정 cardinality는 완전히 다른 최적화 전략을 가능하게 한다.
Vespa의 Per-Token Nearest Neighbor 접근
Phase 0 (Pre-filtering):
각 쿼리 토큰 qᵢ에 대해:
- 이진화 임베딩으로 Hamming 거리 계산
- k₀개 nearest page-patch 검색
- 해당 페이지들의 union 생성
Phase 1 (Approximate MaxSim):
생존 페이지들을 inverted Hamming distance로 스코어링
상위 k₁개 유지
Phase 2 (Exact MaxSim):
상위 k₁개를 full-precision float MaxSim으로 re-rank
Vespa 스타일 ColPali 검색 워크플로우. 이진화 + per-token HNSW + 단계적 reranking.
저장 비용 비교 (10억 페이지 기준):
| 구성 | 페이지당 저장량 | 총 저장량 | Phase 0 Recall |
|---|---|---|---|
| ColPali float32 | 526 KB | ~526 TB | 100% |
| ColPali bfloat16 | 263 KB | ~263 TB | ~99% |
| ColPali binarized | 16.5 KB | ~16.5 TB | ~94% |
| Centroid index (k=30) | 7.7 KB | ~7.7 TB | variable |
32배 압축 + 최소 recall 손실이 핵심이다.
이진화 구현:
def binarize_embeddings(embeddings):
"""각 차원을 평균 기준으로 이진화"""
threshold = embeddings.mean(dim=-1, keepdim=True)
binary = (embeddings > threshold).to(torch.uint8)
# 128 dim → 16 bytes
return torch.packbits(binary, dim=-1)
def hamming_distance(binary1, binary2):
"""Hamming 거리 계산"""
xor = binary1 ^ binary2
return torch.popcnt(xor).sum()
# Per-token HNSW 인덱스
per_token_index = [
hnswlib.Index(space='hamming', dim=16) # 16 bytes
for _ in range(1030) # 각 패치 위치별 인덱스
]
# Phase 0: Per-token nearest neighbor
candidate_pages = set()
for query_token in query_embeddings:
binary_query = binarize_embeddings(query_token)
for token_idx, index in enumerate(per_token_index):
nearest = index.knn_query(binary_query, k=100)
candidate_pages.update(nearest)
# Phase 1: Approximate MaxSim with binary
# Phase 2: Exact MaxSim with float32
의사결정 프레임워크
| 유사도 함수 | 데이터 기하학 | 권장 접근법 | 핵심 고려사항 |
|---|---|---|---|
| SumSim | Any | Mean-pool → 표준 HNSW | Multi-vector 인프라 완전 불필요 |
| MaxSim | Multi-kernel, moderate σ²_intra | PLAID | MS MARCO 스케일에서 검증됨 |
| MaxSim | Multi-kernel, high σ²_intra | PLAID + large codebook | Stage-2 selectivity 실증 검증 필요 |
| MaxSim | Any | MUVERA + re-rank | Recall 검증 필수, b 신중 조정 |
| Top-K Sum | Multi-kernel | 커스텀 파이프라인 | PLAID pruning 직접 적용 불가 |
| MaxSim (ColPali) | High variance, fixed cardinality | Per-token HNSW + 이진화 | 32x 압축, ~94% recall |
| MaxSim (소규모) | <10M 문서 | Brute-force float MaxSim | 특수 인프라 불필요 |
실무 체크리스트:
-
데이터 기하학 먼저 분석:
# Intra-document variance 측정
for doc in corpus:
embeddings = model.encode(doc)
variance = embeddings.var(dim=0).mean()
print(f"σ²_intra = {variance:.4f}")
# Anisotropy 측정 (주성분 분산 비율)
pca = PCA()
pca.fit(all_embeddings)
explained_variance_ratio = pca.explained_variance_ratio_
anisotropy = explained_variance_ratio[0] / explained_variance_ratio[-1] -
유사도 함수 확인: MaxSim이 정말 필요한가? SumSim으로 충분하지 않은가?
-
스케일 고려: 10M 문서 미만이면 brute-force도 실용적
-
고정 cardinality 여부: ColPali 같은 경우 per-token 접근 고려
Embedding Model 설계 시사점
저자의 가장 중요한 통찰: 학습 단계에서 인덱싱 친화적 기하학을 유도할 수 있다.
Intra-document Variance 정규화 (PLAID 최적화)
def variance_regularization_loss(embeddings, target_variance):
"""문서 내 분산을 목표값으로 정규화"""
doc_variance = embeddings.var(dim=0).mean()
return (doc_variance - target_variance) ** 2
# 전체 손실에 추가
total_loss = info_nce_loss + λ_var * variance_reg_loss
σ²_target을 codebook 크기에서 좋은 PLAID selectivity를 보이는 값으로 설정하면, 인덱싱 효율성을 모델에 내재화할 수 있다.
Within-kernel Isotropy 정규화 (MUVERA 최적화)
def isotropy_regularization_loss(embeddings, cluster_assignments):
"""각 클러스터 내에서 등방성 유도"""
loss = 0
for cluster_id in unique(cluster_assignments):
cluster_embeds = embeddings[cluster_assignments == cluster_id]
cov_matrix = torch.cov(cluster_embeds.T)
eigenvalues = torch.linalg.eigvalsh(cov_matrix)
# 고유값 분산 최소화 → 구형 클러스터
loss += eigenvalues.var()
return loss
더 둥근 클러스터 형태를 유도하여 랜덤 하이퍼플레인 파티셔닝과의 호환성 향상.
PoBE(Preference-Optimized Binary Embedding)에의 적용:
class GeometryAwareBinaryEmbedding(nn.Module):
def forward(self, x):
# 표준 임베딩
embeddings = self.encoder(x)
# Variance 정규화 (PLAID용)
var_loss = variance_reg(embeddings, target=0.15)
# Isotropy 정규화 (이진화 친화적)
iso_loss = isotropy_reg(embeddings, self.clusters)
# 이진화
binary_embeds = torch.sign(embeddings - embeddings.mean())
return binary_embeds, var_loss + iso_loss
핵심 메시지: 임베딩 모델 설계와 인덱싱 인프라는 독립적 선택이 아니다. 모델이 학습하는 기하학이 인덱스 성능을 직접 결정하며, 그 기하학에 대한 제어는 일반적으로 인식되는 것보다 훨씬 크다.
열린 연구 질문
Geometry-Aware Hashing
랜덤 하이퍼플레인 대신 실제 공분산 구조 기반 파티셔닝:
- k-means LSH: 주성분 방향으로 파티션
- Learned hashing: 데이터 분포를 직접 학습
Visual Retrieval의 적절한 유사도 함수
ColPali가 MaxSim을 사용하는 것은 ColBERT로부터의 관성일 수 있음:
- 이미지 패치 간 유사도에는 다른 aggregation이 더 적절할 수 있음
- Spatial pooling, attention-weighted sum 등의 대안 탐구 필요
모델 스케일에 따른 기하학 변화
더 큰 모델이 더 isotropic한 임베딩을 생성하는가?
- 표현력 증가가 clustering 구조를 어떻게 변화시키는가?
- 인덱싱 친화도와





